

新疆农业科学 ›› 2022, Vol. 59 ›› Issue (6): 1373-1383.DOI: 10.6048/j.issn.1001-4330.2022.06.008
巴爱丽( ), 杨靖, 贾菲芸, 樊苗苗, 张冉, 李友勇(
), 杨靖, 贾菲芸, 樊苗苗, 张冉, 李友勇( )
)
收稿日期:2021-09-12
出版日期:2022-06-20
发布日期:2022-07-07
通信作者:
李友勇
作者简介:巴爱丽(1988-),女,河南周口人,硕士,研究方向为玉米生物技术,(E-mail) 282657955@qq.com
基金资助:
BA Aili( ), YANG Jing, JIA Feiyun, FAN Miaomiao, ZHANG Ran, LI Youyong(
), YANG Jing, JIA Feiyun, FAN Miaomiao, ZHANG Ran, LI Youyong( )
)
Received:2021-09-12
Online:2022-06-20
Published:2022-07-07
Correspondence author:
LI Youyong
Supported by:摘要:
【目的】 研究玉米杂种优势类群划分高多态SSR引物筛选。【方法】 遴选均匀分布在玉米10个连锁群上160对SSR引物,在104份玉米自交系DNA中扩增,根据引物的染色体分布和PIC值,分别取40、30、20和10对高多态引物建立4套新引物体系,检测104份自交系的分类效果。【结果】 (1)160对引物中的63对引物带型稳定,多态性高,最高PIC值0.762 3,高于过去常用核心SSR引物,63对引物中过去常用核心SSR引物仅保留40%左右;(2)4套引物体系中,40和30对引物体系的分类结果与已知自交系类群高度吻合,20对体系与40对体系比较具90.5%一致性,10对体系与40对体系比较的一致性81.0%;(3)40对体系分类104份材料为5大类群,分别是瑞德、改良瑞德、兰卡斯特、黄改和和旅大红骨,与目前国内利用的优势群划分结果一致,也能鉴别出每个群中亲缘关系最远的亚群是相近群间二环系来源的混合基因型;(4) 各群的代表自交系是单一遗传结构成分,亚群是多遗传结构成分。【结论】 部分SSR引物的多态性在新自交系中会出现下降,建立的新的40对引物体系有精确的分类功能,可应用于类群划分,20对体系的分类精确性稍低,但检测工作量减半,在批量材料分类中有利用价值。
中图分类号:
巴爱丽, 杨靖, 贾菲芸, 樊苗苗, 张冉, 李友勇. 玉米杂种优势类群划分高多态SSR引物筛选[J]. 新疆农业科学, 2022, 59(6): 1373-1383.
BA Aili, YANG Jing, JIA Feiyun, FAN Miaomiao, ZHANG Ran, LI Youyong. Screening of High Polymorphism SSR Primers for Classification of Heterosis Group in Maize (Zea mays L.)[J]. Xinjiang Agricultural Sciences, 2022, 59(6): 1373-1383.
| 序号 No. | 自交系名称 Inbred line name | 来源 Resources | 序号 No. | 自交系名称 Inbred line name | 种质 Germplasm |
|---|---|---|---|---|---|
| 1 | PH6WC-1 | PH6WC | 53 | HPH4CV | PH4CV改良系 |
| 2 | PH6WC-2 | PH6WC改良系 | 54 | L16-1 | 二环系 |
| 3 | PH6WC-3 | PH6WC改良系 | 55 | MS001 | 旅系改良系 |
| 4 | X35 | PH6WC改良系 | 56 | 京66 | 华农138♂ |
| 5 | CF30 | 自选改良系 | 57 | MC712 | 滑玉168♂ |
| 6 | PHBIM | DH516♂ | 58 | KWS | 兰卡 |
| 7 | HCL645 | 迪卡517♂ | 59 | 合5002-3 | 改良Reid系 |
| 8 | PH6WC-4 | PH6WC改良系 | 60 | 17郑58 | 郑58 |
| 9 | PH1CPS | 先玉1111♀ | 61 | 臣718 | 改良Reid |
| 10 | V69-1 | Reid改良系 | 62 | V69-2 | 改良Reid |
| 11 | 改郑58-2 | 郑58改良系 | 63 | 易选-2 | 改良兰卡 |
| 12 | 14郑58 | 郑58 | 64 | D2-2 | 改良兰卡 |
| 13 | 457-1 | 武克2号♀ | 65 | D2-3 | 改良兰卡 |
| 序号 No. | 自交系名称 Inbred line name | 来源 Resources | 序号 No. | 自交系名称 Inbred line name | 种质 Germplasm |
| 14 | 合5002-1 | 自选Reid系 | 66 | 改8752-2 | 自选Reid系 |
| 15 | D2-1 | 改良兰卡 | 67 | 18郑58 | 郑58 |
| 16 | 改8752-1 | 自选Reid系 | 68 | 18昌7-2 | 昌7-2 |
| 17 | 改郑58-1 | 郑58改良系 | 69 | D2-4 | 自选黄改系 |
| 18 | 利玛格兰 | 利玛格兰选系 | 70 | 浚92-6 | 浚单♂ |
| 19 | 合5002-2 | 自选Reid系 | 71 | 14昌7-2 | 昌7-2 |
| 20 | M54 | 良玉88♀ | 72 | PH6G-1 | PH6改良系 |
| 21 | 浚326 | 浚单20♂ | 73 | PH6G-2 | PH6WC改良系 |
| 22 | 黄01 | 自选黄改系 | 74 | PH6G-3 | PH6WC改良系 |
| 23 | 郑22优 | 武科2号♂ | 75 | 12Y10S-3 | 群间二环系 |
| 24 | 浚92-6 | 浚单18♂ | 76 | LD1 | 群间二环系 |
| 25 | 370-1 | 自选黄改系 | 77 | J19-2 | 群间自选系 |
| 26 | WK798-2 | 伟科702 ♂ | 78 | CF31 | 群间自选系 |
| 27 | 郑22 | 黄改系 | 79 | J19-3 | 群间自选系 |
| 28 | 浚92-8 | 浚单26♂ | 80 | LD2 | 群间自选系 |
| 29 | FW1 | 改良兰卡 | 81 | 12Y09 | 群间自选系 |
| 30 | PH4CV-1 | 兰卡 | 82 | S91D2 | 改良兰卡 |
| 31 | PH4CV恢 | PH6WC恢复系 | 83 | T170370 | 黄改 |
| 32 | PH4CV-2 | PH4CV改良系 | 84 | A01-1 | 自选改良Reid |
| 33 | 臣PH4CV | PH4CV改良系 | 85 | J19 | 改良Reid |
| 34 | PH4CV-4 | PH4CV改良系 | 86 | 543PH6 | PH6WC改良系 |
| 35 | PH4CV-3 | PH4CV改良系 | 87 | 886FPH4 | PH4CV改良系 |
| 36 | CPH4CV | PH4CV改良系 | 88 | 517F | 517改良系 |
| 37 | GPH4CV | PH4CV改良系 | 89 | S72702F | 黄改系 |
| 38 | ZPH4CV | PH4CV改良系 | 90 | T94 | 黄改系 |
| 39 | 改MS001 | MS001改良系 | 91 | W517F | 517改良系 |
| 40 | 宏198 | 宏硬198♀ | 92 | T95 | 黄改系 |
| 41 | W245 | 引自东北 | 93 | T168370 | 黄改系 |
| 42 | W246 | 引自东北 | 94 | T158D2 | 改良兰卡 |
| 43 | E28 | 旅大红骨 | 95 | RPH6 | Reid改良系 |
| 44 | 改X35 | PH6WC改良系 | 96 | 926S122 | 黄改类 |
| 45 | 改PH6WC1 | PH6WC改良系 | 97 | T89 | 黄改类 |
| 46 | 改PH6WC2 | PH6WC改良系 | 98 | 凤仙 | 改良Reid |
| 47 | 12Y10S-1 | 群间二环系 | 99 | 16N03 | 改良Reid |
| 48 | 12Y10S-2 | 群间二环系 | 100 | 543PH61 | 群间二环系 |
| 49 | G7B159 | 德1209♀ | 101 | Lanca | Lacaune系 |
| 50 | 7B159 | 德129♀ | 102 | T517F | 517改良系 |
| 51 | 罗W28 | 瑞德 | 103 | C517F | 517改良系 |
| 52 | PH4CV-5 | PH4CV改良系 | 104 | A168752 | 改良Reid |
表1 104份玉米自交系名称及种质亲缘
Table 1 The names of 104 maize inbred lines and their germplasm relatives
| 序号 No. | 自交系名称 Inbred line name | 来源 Resources | 序号 No. | 自交系名称 Inbred line name | 种质 Germplasm |
|---|---|---|---|---|---|
| 1 | PH6WC-1 | PH6WC | 53 | HPH4CV | PH4CV改良系 |
| 2 | PH6WC-2 | PH6WC改良系 | 54 | L16-1 | 二环系 |
| 3 | PH6WC-3 | PH6WC改良系 | 55 | MS001 | 旅系改良系 |
| 4 | X35 | PH6WC改良系 | 56 | 京66 | 华农138♂ |
| 5 | CF30 | 自选改良系 | 57 | MC712 | 滑玉168♂ |
| 6 | PHBIM | DH516♂ | 58 | KWS | 兰卡 |
| 7 | HCL645 | 迪卡517♂ | 59 | 合5002-3 | 改良Reid系 |
| 8 | PH6WC-4 | PH6WC改良系 | 60 | 17郑58 | 郑58 |
| 9 | PH1CPS | 先玉1111♀ | 61 | 臣718 | 改良Reid |
| 10 | V69-1 | Reid改良系 | 62 | V69-2 | 改良Reid |
| 11 | 改郑58-2 | 郑58改良系 | 63 | 易选-2 | 改良兰卡 |
| 12 | 14郑58 | 郑58 | 64 | D2-2 | 改良兰卡 |
| 13 | 457-1 | 武克2号♀ | 65 | D2-3 | 改良兰卡 |
| 序号 No. | 自交系名称 Inbred line name | 来源 Resources | 序号 No. | 自交系名称 Inbred line name | 种质 Germplasm |
| 14 | 合5002-1 | 自选Reid系 | 66 | 改8752-2 | 自选Reid系 |
| 15 | D2-1 | 改良兰卡 | 67 | 18郑58 | 郑58 |
| 16 | 改8752-1 | 自选Reid系 | 68 | 18昌7-2 | 昌7-2 |
| 17 | 改郑58-1 | 郑58改良系 | 69 | D2-4 | 自选黄改系 |
| 18 | 利玛格兰 | 利玛格兰选系 | 70 | 浚92-6 | 浚单♂ |
| 19 | 合5002-2 | 自选Reid系 | 71 | 14昌7-2 | 昌7-2 |
| 20 | M54 | 良玉88♀ | 72 | PH6G-1 | PH6改良系 |
| 21 | 浚326 | 浚单20♂ | 73 | PH6G-2 | PH6WC改良系 |
| 22 | 黄01 | 自选黄改系 | 74 | PH6G-3 | PH6WC改良系 |
| 23 | 郑22优 | 武科2号♂ | 75 | 12Y10S-3 | 群间二环系 |
| 24 | 浚92-6 | 浚单18♂ | 76 | LD1 | 群间二环系 |
| 25 | 370-1 | 自选黄改系 | 77 | J19-2 | 群间自选系 |
| 26 | WK798-2 | 伟科702 ♂ | 78 | CF31 | 群间自选系 |
| 27 | 郑22 | 黄改系 | 79 | J19-3 | 群间自选系 |
| 28 | 浚92-8 | 浚单26♂ | 80 | LD2 | 群间自选系 |
| 29 | FW1 | 改良兰卡 | 81 | 12Y09 | 群间自选系 |
| 30 | PH4CV-1 | 兰卡 | 82 | S91D2 | 改良兰卡 |
| 31 | PH4CV恢 | PH6WC恢复系 | 83 | T170370 | 黄改 |
| 32 | PH4CV-2 | PH4CV改良系 | 84 | A01-1 | 自选改良Reid |
| 33 | 臣PH4CV | PH4CV改良系 | 85 | J19 | 改良Reid |
| 34 | PH4CV-4 | PH4CV改良系 | 86 | 543PH6 | PH6WC改良系 |
| 35 | PH4CV-3 | PH4CV改良系 | 87 | 886FPH4 | PH4CV改良系 |
| 36 | CPH4CV | PH4CV改良系 | 88 | 517F | 517改良系 |
| 37 | GPH4CV | PH4CV改良系 | 89 | S72702F | 黄改系 |
| 38 | ZPH4CV | PH4CV改良系 | 90 | T94 | 黄改系 |
| 39 | 改MS001 | MS001改良系 | 91 | W517F | 517改良系 |
| 40 | 宏198 | 宏硬198♀ | 92 | T95 | 黄改系 |
| 41 | W245 | 引自东北 | 93 | T168370 | 黄改系 |
| 42 | W246 | 引自东北 | 94 | T158D2 | 改良兰卡 |
| 43 | E28 | 旅大红骨 | 95 | RPH6 | Reid改良系 |
| 44 | 改X35 | PH6WC改良系 | 96 | 926S122 | 黄改类 |
| 45 | 改PH6WC1 | PH6WC改良系 | 97 | T89 | 黄改类 |
| 46 | 改PH6WC2 | PH6WC改良系 | 98 | 凤仙 | 改良Reid |
| 47 | 12Y10S-1 | 群间二环系 | 99 | 16N03 | 改良Reid |
| 48 | 12Y10S-2 | 群间二环系 | 100 | 543PH61 | 群间二环系 |
| 49 | G7B159 | 德1209♀ | 101 | Lanca | Lacaune系 |
| 50 | 7B159 | 德129♀ | 102 | T517F | 517改良系 |
| 51 | 罗W28 | 瑞德 | 103 | C517F | 517改良系 |
| 52 | PH4CV-5 | PH4CV改良系 | 104 | A168752 | 改良Reid |
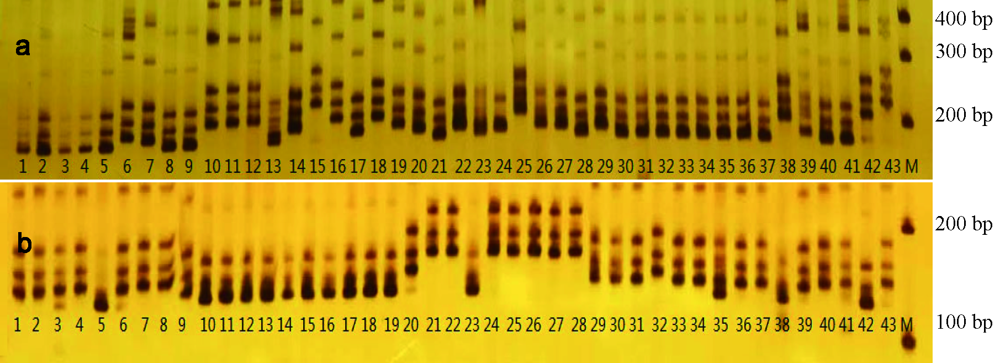
图1 两个引物(a, bnlg1702,和b, umc1084)在部分玉米自交系DNA中的扩增SSR图谱
Fig.1 SSR gel graphs amplified by both of primers(a, bnlg1702, and b, umc1084) in DNA of partial maize inbred lines
| 序号 No. | 引物体系 Primer system | 引物遗传参数 Genetic parameter of each primer | ||||||
|---|---|---|---|---|---|---|---|---|
| 40对 40 pairs | 30对 30 pairs | 20对 20 pairs | 10对 10 pairs | 染色体位置 Bin | 等位基因数 Allele No. | 基因多样性 Gene diversity | PIC值 PIC value | |
| 1 | bnlg1671 | √ | √ | 1.10 | 4 | 0.731 2 | 0.680 9 | |
| 2 | phi064 | √ | 1.11 | 4 | 0.696 6 | 0.637 9 | ||
| 3 | bnlg1083 | 1.02 | 3 | 0.618 7 | 0.540 0 | |||
| 4 | bnlg2331 | √ | √ | √ | 1.11 | 5 | 0.743 1 | 0.700 5 |
| 5 | bnlg125 | 2.02 | 3 | 0.639 3 | 0.564 0 | |||
| 6 | bnlg198 | √ | √ | √ | 2.08 | 3 | 0.640 3 | 0.568 1 |
| 7 | umc2007 | √ | 2.04 | 5 | 0.699 8 | 0.654 2 | ||
| 8 | dupssr24 | √ | √ | 2.08 | 4 | 0.600 3 | 0.556 4 | |
| 9 | umc2105 | √ | √ | 3.00 | 4 | 0.641 4 | 0.596 5 | |
| 10 | bnlg2241 | 3.04 | 3 | 0.649 0 | 0.576 0 | |||
| 11 | bnlg1754 | √ | √ | √ | 3.09 | 4 | 0.683 6 | 0.629 0 |
| 12 | phi053 | √ | 3.05 | 4 | 0.705 2 | 0.654 9 | ||
| 13 | umc1808 | √ | √ | √ | 4.08 | 4 | 0.733 4 | 0.684 3 |
| 14 | bnlg589 | 4.10 | 3 | 0.562 5 | 0.464 7 | |||
| 15 | umc1294 | √ | 4.02 | 3 | 0.564 6 | 0.495 8 | ||
| 16 | umc2082 | √ | √ | 4.03 | 3 | 0.603 6 | 0.522 8 | |
| 17 | bnlg1006 | √ | 5.00 | 4 | 0.742 0 | 0.694 5 | ||
| 18 | umc1056 | √ | √ | 5.03 | 6 | 0.777 7 | 0.741 1 | |
| 19 | bnlg238 | 5.06 | 3 | 0.653 3 | 0.579 4 | |||
| 20 | umc1705 | √ | √ | √ | 5.03 | 5 | 0.795 0 | 0.762 3 |
| 21 | bnlg1702 | √ | √ | √ | 6.05 | 6 | 0.777 7 | 0.749 3 |
| 22 | phi126 | 6.00 | 4 | 0.683 6 | 0.634 3 | |||
| 23 | bnlg84 | √ | √ | 6.00 | 4 | 0.725 8 | 0.676 7 | |
| 24 | bnlg161 | √ | 6.00 | 4 | 0.700 9 | 0.646 2 | ||
| 25 | umc2331 | √ | √ | √ | 7.04 | 5 | 0.658 7 | 0.624 9 |
| 26 | phi328175 | √ | 7.04 | 3 | 0.620 9 | 0.546 5 | ||
| 27 | umc1710 | 7.04 | 3 | 0.573 3 | 0.484 2 | |||
| 28 | phi015 | √ | √ | 7.06 | 3 | 0.644 7 | 0.570 7 | |
| 29 | umc1741 | √ | √ | 8.03 | 4 | 0.663 1 | 0.598 8 | |
| 30 | bnlg1863 | √ | 8.03 | 4 | 0.673 9 | 0.605 8 | ||
| 31 | bnlg240 | √ | √ | √ | 8.05 | 4 | 0.697 7 | 0.648 6 |
| 32 | phi080 | 8.08 | 3 | 0.662 0 | 0.587 8 | |||
| 33 | umc2084 | √ | √ | √ | 9.01 | 4 | 0.696 6 | 0.647 2 |
| 34 | umc1033 | √ | √ | 9.02 | 4 | 0.687 9 | 0.634 6 | |
| 35 | bnlg1012 | √ | 9.05 | 4 | 0.662 0 | 0.601 7 | ||
| 36 | umc1231 | 9.05 | 3 | 0.647 9 | 0.574 7 | |||
| 37 | umc1239 | 10.03 | 3 | 0.653 3 | 0.579 4 | |||
| 38 | umc2163 | √ | √ | √ | 10.04 | 4 | 0.742 0 | 0.694 5 |
| 39 | bnlg1450 | √ | 10.07 | 3 | 0.662 0 | 0.587 8 | ||
| 40 | umc1084 | √ | √ | 10.07 | 4 | 0.722 6 | 0.672 7 | |
表2 遴选的4套引物及遗传参数
Table 2 Selected 4 sets of primers and their genetic parameters
| 序号 No. | 引物体系 Primer system | 引物遗传参数 Genetic parameter of each primer | ||||||
|---|---|---|---|---|---|---|---|---|
| 40对 40 pairs | 30对 30 pairs | 20对 20 pairs | 10对 10 pairs | 染色体位置 Bin | 等位基因数 Allele No. | 基因多样性 Gene diversity | PIC值 PIC value | |
| 1 | bnlg1671 | √ | √ | 1.10 | 4 | 0.731 2 | 0.680 9 | |
| 2 | phi064 | √ | 1.11 | 4 | 0.696 6 | 0.637 9 | ||
| 3 | bnlg1083 | 1.02 | 3 | 0.618 7 | 0.540 0 | |||
| 4 | bnlg2331 | √ | √ | √ | 1.11 | 5 | 0.743 1 | 0.700 5 |
| 5 | bnlg125 | 2.02 | 3 | 0.639 3 | 0.564 0 | |||
| 6 | bnlg198 | √ | √ | √ | 2.08 | 3 | 0.640 3 | 0.568 1 |
| 7 | umc2007 | √ | 2.04 | 5 | 0.699 8 | 0.654 2 | ||
| 8 | dupssr24 | √ | √ | 2.08 | 4 | 0.600 3 | 0.556 4 | |
| 9 | umc2105 | √ | √ | 3.00 | 4 | 0.641 4 | 0.596 5 | |
| 10 | bnlg2241 | 3.04 | 3 | 0.649 0 | 0.576 0 | |||
| 11 | bnlg1754 | √ | √ | √ | 3.09 | 4 | 0.683 6 | 0.629 0 |
| 12 | phi053 | √ | 3.05 | 4 | 0.705 2 | 0.654 9 | ||
| 13 | umc1808 | √ | √ | √ | 4.08 | 4 | 0.733 4 | 0.684 3 |
| 14 | bnlg589 | 4.10 | 3 | 0.562 5 | 0.464 7 | |||
| 15 | umc1294 | √ | 4.02 | 3 | 0.564 6 | 0.495 8 | ||
| 16 | umc2082 | √ | √ | 4.03 | 3 | 0.603 6 | 0.522 8 | |
| 17 | bnlg1006 | √ | 5.00 | 4 | 0.742 0 | 0.694 5 | ||
| 18 | umc1056 | √ | √ | 5.03 | 6 | 0.777 7 | 0.741 1 | |
| 19 | bnlg238 | 5.06 | 3 | 0.653 3 | 0.579 4 | |||
| 20 | umc1705 | √ | √ | √ | 5.03 | 5 | 0.795 0 | 0.762 3 |
| 21 | bnlg1702 | √ | √ | √ | 6.05 | 6 | 0.777 7 | 0.749 3 |
| 22 | phi126 | 6.00 | 4 | 0.683 6 | 0.634 3 | |||
| 23 | bnlg84 | √ | √ | 6.00 | 4 | 0.725 8 | 0.676 7 | |
| 24 | bnlg161 | √ | 6.00 | 4 | 0.700 9 | 0.646 2 | ||
| 25 | umc2331 | √ | √ | √ | 7.04 | 5 | 0.658 7 | 0.624 9 |
| 26 | phi328175 | √ | 7.04 | 3 | 0.620 9 | 0.546 5 | ||
| 27 | umc1710 | 7.04 | 3 | 0.573 3 | 0.484 2 | |||
| 28 | phi015 | √ | √ | 7.06 | 3 | 0.644 7 | 0.570 7 | |
| 29 | umc1741 | √ | √ | 8.03 | 4 | 0.663 1 | 0.598 8 | |
| 30 | bnlg1863 | √ | 8.03 | 4 | 0.673 9 | 0.605 8 | ||
| 31 | bnlg240 | √ | √ | √ | 8.05 | 4 | 0.697 7 | 0.648 6 |
| 32 | phi080 | 8.08 | 3 | 0.662 0 | 0.587 8 | |||
| 33 | umc2084 | √ | √ | √ | 9.01 | 4 | 0.696 6 | 0.647 2 |
| 34 | umc1033 | √ | √ | 9.02 | 4 | 0.687 9 | 0.634 6 | |
| 35 | bnlg1012 | √ | 9.05 | 4 | 0.662 0 | 0.601 7 | ||
| 36 | umc1231 | 9.05 | 3 | 0.647 9 | 0.574 7 | |||
| 37 | umc1239 | 10.03 | 3 | 0.653 3 | 0.579 4 | |||
| 38 | umc2163 | √ | √ | √ | 10.04 | 4 | 0.742 0 | 0.694 5 |
| 39 | bnlg1450 | √ | 10.07 | 3 | 0.662 0 | 0.587 8 | ||
| 40 | umc1084 | √ | √ | 10.07 | 4 | 0.722 6 | 0.672 7 | |
| 类群 Group | 自交系数目 Number of inbred lines | ||||
|---|---|---|---|---|---|
| 已知类群 Known groups | 40对体系 40 pairs of system | 30对体系 30 pairs of system | 20对体系 20 pairs of system | 10对体系 10 pairs of system | |
| 瑞德Reid | 8 | 8 | 9 | 6 | 12 |
| 改良瑞德Improved Reid | 12 | 12 | 13 | 16 | 11 |
| 兰卡斯特Lancaster | 11 | 11 | 10 | 10 | 8 |
| 黄改Improved Huang | 11 | 11 | 10 | 10 | 11 |
| 总数Total | 42 | 42 | 42 | 42 | 42 |
表3 4套引物体系分类42份玉米自交系的类群及类群内的自交系数目
Table 3 The groups and the number of inbred lines in each group, classification of 42 inbred lines by 4 sets of primer systems
| 类群 Group | 自交系数目 Number of inbred lines | ||||
|---|---|---|---|---|---|
| 已知类群 Known groups | 40对体系 40 pairs of system | 30对体系 30 pairs of system | 20对体系 20 pairs of system | 10对体系 10 pairs of system | |
| 瑞德Reid | 8 | 8 | 9 | 6 | 12 |
| 改良瑞德Improved Reid | 12 | 12 | 13 | 16 | 11 |
| 兰卡斯特Lancaster | 11 | 11 | 10 | 10 | 8 |
| 黄改Improved Huang | 11 | 11 | 10 | 10 | 11 |
| 总数Total | 42 | 42 | 42 | 42 | 42 |
| 自交系名称 Name of inbred lines | 遗传组成Genetic composition | ||||||
|---|---|---|---|---|---|---|---|
| 瑞德 Reid | 改良瑞德 Improved Reid | 兰卡斯特 Lancaster | 拟兰卡斯特 Like-Lancaster | 旅大红骨 Mixtures | 黄改 Improved Huang | 拟黄改 Like-Huang | |
| PH6WC-1 | 0.987 9 | 0.001 9 | 0.002 0 | 0.002 0 | 0.002 3 | 0.001 9 | 0.002 0 |
| PH6WC-2 | 0.988 3 | 0.001 5 | 0.002 0 | 0.002 0 | 0.002 3 | 0.001 9 | 0.002 0 |
| X35 | 0.983 1 | 0.002 0 | 0.002 0 | 0.002 0 | 0.006 0 | 0.002 9 | 0.002 0 |
| HCL645 | 0.987 7 | 0.003 0 | 0.002 4 | 0.001 3 | 0.002 0 | 0.001 4 | 0.002 2 |
| PH6WC-4 | 0.987 8 | 0.002 8 | 0.002 4 | 0.001 3 | 0.002 0 | 0.001 4 | 0.002 3 |
| 改PH6WC1 | 0.967 9 | 0.002 0 | 0.003 6 | 0.004 5 | 0.002 2 | 0.002 1 | 0.017 7 |
| PH6G-1 | 0.940 3 | 0.007 3 | 0.037 4 | 0.003 6 | 0.003 2 | 0.002 0 | 0.006 2 |
| W246 | 0.003 3 | 0.015 3 | 0.016 2 | 0.005 9 | 0.946 1 | 0.007 7 | 0.005 5 |
| E28 | 0.002 0 | 0.003 2 | 0.056 4 | 0.015 3 | 0.910 2 | 0.006 5 | 0.006 4 |
| 改PH6WC2 | 0.124 3 | 0.002 7 | 0.003 2 | 0.009 9 | 0.853 6 | 0.003 1 | 0.003 2 |
| 12Y10S-2 | 0.021 0 | 0.040 5 | 0.004 7 | 0.003 7 | 0.924 9 | 0.002 4 | 0.002 8 |
| LD2 | 0.087 6 | 0.012 4 | 0.007 5 | 0.003 1 | 0.878 6 | 0.005 8 | 0.005 0 |
| J19-1 | 0.002 0 | 0.026 6 | 0.004 3 | 0.002 6 | 0.959 9 | 0.002 3 | 0.002 3 |
| T158D2 | 0.004 6 | 0.020 8 | 0.002 7 | 0.002 0 | 0.963 8 | 0.002 7 | 0.003 4 |
| V69-1 | 0.002 3 | 0.954 7 | 0.028 6 | 0.007 9 | 0.003 7 | 0.001 3 | 0.001 5 |
| 14郑58 | 0.002 0 | 0.985 5 | 0.002 9 | 0.002 6 | 0.003 7 | 0.001 3 | 0.002 0 |
| 457-1 | 0.005 2 | 0.864 4 | 0.096 6 | 0.003 1 | 0.024 4 | 0.002 8 | 0.003 5 |
| 合5002-1 | 0.013 0 | 0.858 6 | 0.069 1 | 0.002 0 | 0.051 1 | 0.002 0 | 0.004 2 |
| 臣718 | 0.059 3 | 0.820 1 | 0.007 6 | 0.100 8 | 0.006 3 | 0.002 0 | 0.003 9 |
| D2-3 | 0.001 9 | 0.972 0 | 0.011 0 | 0.008 1 | 0.003 0 | 0.002 0 | 0.002 0 |
| 自交系名称 Name of inbred lines | 遗传组成Genetic composition | ||||||
| 瑞德 Reid | 改良瑞德 Improved Reid | 兰卡斯特 Lancaster | 拟兰卡斯特 Like-Lancaster | 旅大红骨 Mixtures | 黄改 Improved Huang | 拟黄改 Like-Huang | |
| 18郑58 | 0.002 0 | 0.987 9 | 0.002 3 | 0.002 0 | 0.002 5 | 0.001 3 | 0.002 0 |
| PH4CV-1 | 0.002 2 | 0.002 3 | 0.621 5 | 0.365 8 | 0.002 1 | 0.002 2 | 0.003 9 |
| PH4CV恢 | 0.005 5 | 0.002 3 | 0.618 4 | 0.330 0 | 0.013 2 | 0.004 9 | 0.025 7 |
| 臣PH4CV | 0.001 5 | 0.002 0 | 0.620 1 | 0.370 1 | 0.002 0 | 0.002 0 | 0.002 3 |
| PH4CV-4 | 0.018 9 | 0.002 3 | 0.606 0 | 0.350 4 | 0.002 3 | 0.002 1 | 0.018 1 |
| GPH4CV | 0.023 1 | 0.003 1 | 0.594 0 | 0.172 3 | 0.114 8 | 0.089 1 | 0.003 5 |
| 宏198 | 0.007 3 | 0.043 5 | 0.624 8 | 0.258 1 | 0.014 5 | 0.002 0 | 0.049 8 |
| G7B159 | 0.101 0 | 0.005 6 | 0.011 2 | 0.823 8 | 0.040 6 | 0.008 0 | 0.009 8 |
| 罗W28 | 0.242 3 | 0.002 7 | 0.006 0 | 0.734 0 | 0.006 2 | 0.004 1 | 0.004 7 |
| PH4CV-5 | 0.001 4 | 0.002 0 | 0.012 7 | 0.972 8 | 0.002 3 | 0.005 3 | 0.003 5 |
| HPH4CV | 0.033 1 | 0.004 8 | 0.038 5 | 0.794 4 | 0.109 5 | 0.014 3 | 0.005 3 |
| 京66 | 0.002 0 | 0.002 2 | 0.003 4 | 0.987 1 | 0.002 0 | 0.001 3 | 0.002 0 |
| MC712 | 0.006 0 | 0.006 1 | 0.125 7 | 0.855 6 | 0.002 9 | 0.001 5 | 0.002 2 |
| 浚326 | 0.002 0 | 0.019 4 | 0.005 9 | 0.003 7 | 0.006 2 | 0.957 8 | 0.005 0 |
| 黄01 | 0.004 1 | 0.004 3 | 0.002 2 | 0.001 6 | 0.003 2 | 0.964 7 | 0.019 9 |
| 370-1 | 0.001 8 | 0.002 0 | 0.010 5 | 0.016 7 | 0.004 7 | 0.954 0 | 0.010 3 |
| 郑22 | 0.001 9 | 0.001 6 | 0.001 8 | 0.001 3 | 0.002 2 | 0.988 9 | 0.002 3 |
| 浚92-8 | 0.003 0 | 0.003 6 | 0.002 7 | 0.002 0 | 0.003 0 | 0.976 2 | 0.009 5 |
| S72702 | 0.003 0 | 0.001 4 | 0.002 2 | 0.001 8 | 0.003 9 | 0.985 4 | 0.002 3 |
| T94 | 0.002 0 | 0.001 3 | 0.001 9 | 0.001 6 | 0.002 0 | 0.989 2 | 0.002 0 |
| 12Y10S-1 | 0.378 4 | 0.010 5 | 0.036 6 | 0.003 0 | 0.021 2 | 0.545 7 | 0.004 6 |
| 12Y10S-3 | 0.089 0 | 0.019 5 | 0.413 8 | 0.152 6 | 0.270 7 | 0.039 0 | 0.015 5 |
| PH1CPS | 0.063 7 | 0.221 5 | 0.032 2 | 0.386 9 | 0.002 6 | 0.002 0 | 0.291 1 |
| ZPH4CV | 0.015 2 | 0.037 2 | 0.283 4 | 0.278 2 | 0.009 6 | 0.334 2 | 0.042 3 |
| 改MS001 | 0.178 4 | 0.327 0 | 0.029 3 | 0.429 7 | 0.004 3 | 0.011 7 | 0.019 5 |
| L16-1 | 0.005 6 | 0.046 4 | 0.014 1 | 0.003 0 | 0.162 6 | 0.360 0 | 0.408 3 |
| 易选-2 | 0.141 7 | 0.279 9 | 0.028 7 | 0.037 5 | 0.010 6 | 0.086 5 | 0.415 1 |
| 12Y10S-3 | 0.015 5 | 0.089 0 | 0.413 8 | 0.270 7 | 0.152 6 | 0.039 0 | 0.019 5 |
| D2-5 | 0.015 0 | 0.009 8 | 0.356 8 | 0.180 2 | 0.186 1 | 0.002 3 | 0.249 8 |
| 543PH62 | 0.003 9 | 0.308 2 | 0.250 2 | 0.229 4 | 0.120 0 | 0.003 2 | 0.085 1 |
表4 104份材料中部分典型自交系的群体遗传组成
Table 4 Population genetic composition of partial of 104 inbred lines
| 自交系名称 Name of inbred lines | 遗传组成Genetic composition | ||||||
|---|---|---|---|---|---|---|---|
| 瑞德 Reid | 改良瑞德 Improved Reid | 兰卡斯特 Lancaster | 拟兰卡斯特 Like-Lancaster | 旅大红骨 Mixtures | 黄改 Improved Huang | 拟黄改 Like-Huang | |
| PH6WC-1 | 0.987 9 | 0.001 9 | 0.002 0 | 0.002 0 | 0.002 3 | 0.001 9 | 0.002 0 |
| PH6WC-2 | 0.988 3 | 0.001 5 | 0.002 0 | 0.002 0 | 0.002 3 | 0.001 9 | 0.002 0 |
| X35 | 0.983 1 | 0.002 0 | 0.002 0 | 0.002 0 | 0.006 0 | 0.002 9 | 0.002 0 |
| HCL645 | 0.987 7 | 0.003 0 | 0.002 4 | 0.001 3 | 0.002 0 | 0.001 4 | 0.002 2 |
| PH6WC-4 | 0.987 8 | 0.002 8 | 0.002 4 | 0.001 3 | 0.002 0 | 0.001 4 | 0.002 3 |
| 改PH6WC1 | 0.967 9 | 0.002 0 | 0.003 6 | 0.004 5 | 0.002 2 | 0.002 1 | 0.017 7 |
| PH6G-1 | 0.940 3 | 0.007 3 | 0.037 4 | 0.003 6 | 0.003 2 | 0.002 0 | 0.006 2 |
| W246 | 0.003 3 | 0.015 3 | 0.016 2 | 0.005 9 | 0.946 1 | 0.007 7 | 0.005 5 |
| E28 | 0.002 0 | 0.003 2 | 0.056 4 | 0.015 3 | 0.910 2 | 0.006 5 | 0.006 4 |
| 改PH6WC2 | 0.124 3 | 0.002 7 | 0.003 2 | 0.009 9 | 0.853 6 | 0.003 1 | 0.003 2 |
| 12Y10S-2 | 0.021 0 | 0.040 5 | 0.004 7 | 0.003 7 | 0.924 9 | 0.002 4 | 0.002 8 |
| LD2 | 0.087 6 | 0.012 4 | 0.007 5 | 0.003 1 | 0.878 6 | 0.005 8 | 0.005 0 |
| J19-1 | 0.002 0 | 0.026 6 | 0.004 3 | 0.002 6 | 0.959 9 | 0.002 3 | 0.002 3 |
| T158D2 | 0.004 6 | 0.020 8 | 0.002 7 | 0.002 0 | 0.963 8 | 0.002 7 | 0.003 4 |
| V69-1 | 0.002 3 | 0.954 7 | 0.028 6 | 0.007 9 | 0.003 7 | 0.001 3 | 0.001 5 |
| 14郑58 | 0.002 0 | 0.985 5 | 0.002 9 | 0.002 6 | 0.003 7 | 0.001 3 | 0.002 0 |
| 457-1 | 0.005 2 | 0.864 4 | 0.096 6 | 0.003 1 | 0.024 4 | 0.002 8 | 0.003 5 |
| 合5002-1 | 0.013 0 | 0.858 6 | 0.069 1 | 0.002 0 | 0.051 1 | 0.002 0 | 0.004 2 |
| 臣718 | 0.059 3 | 0.820 1 | 0.007 6 | 0.100 8 | 0.006 3 | 0.002 0 | 0.003 9 |
| D2-3 | 0.001 9 | 0.972 0 | 0.011 0 | 0.008 1 | 0.003 0 | 0.002 0 | 0.002 0 |
| 自交系名称 Name of inbred lines | 遗传组成Genetic composition | ||||||
| 瑞德 Reid | 改良瑞德 Improved Reid | 兰卡斯特 Lancaster | 拟兰卡斯特 Like-Lancaster | 旅大红骨 Mixtures | 黄改 Improved Huang | 拟黄改 Like-Huang | |
| 18郑58 | 0.002 0 | 0.987 9 | 0.002 3 | 0.002 0 | 0.002 5 | 0.001 3 | 0.002 0 |
| PH4CV-1 | 0.002 2 | 0.002 3 | 0.621 5 | 0.365 8 | 0.002 1 | 0.002 2 | 0.003 9 |
| PH4CV恢 | 0.005 5 | 0.002 3 | 0.618 4 | 0.330 0 | 0.013 2 | 0.004 9 | 0.025 7 |
| 臣PH4CV | 0.001 5 | 0.002 0 | 0.620 1 | 0.370 1 | 0.002 0 | 0.002 0 | 0.002 3 |
| PH4CV-4 | 0.018 9 | 0.002 3 | 0.606 0 | 0.350 4 | 0.002 3 | 0.002 1 | 0.018 1 |
| GPH4CV | 0.023 1 | 0.003 1 | 0.594 0 | 0.172 3 | 0.114 8 | 0.089 1 | 0.003 5 |
| 宏198 | 0.007 3 | 0.043 5 | 0.624 8 | 0.258 1 | 0.014 5 | 0.002 0 | 0.049 8 |
| G7B159 | 0.101 0 | 0.005 6 | 0.011 2 | 0.823 8 | 0.040 6 | 0.008 0 | 0.009 8 |
| 罗W28 | 0.242 3 | 0.002 7 | 0.006 0 | 0.734 0 | 0.006 2 | 0.004 1 | 0.004 7 |
| PH4CV-5 | 0.001 4 | 0.002 0 | 0.012 7 | 0.972 8 | 0.002 3 | 0.005 3 | 0.003 5 |
| HPH4CV | 0.033 1 | 0.004 8 | 0.038 5 | 0.794 4 | 0.109 5 | 0.014 3 | 0.005 3 |
| 京66 | 0.002 0 | 0.002 2 | 0.003 4 | 0.987 1 | 0.002 0 | 0.001 3 | 0.002 0 |
| MC712 | 0.006 0 | 0.006 1 | 0.125 7 | 0.855 6 | 0.002 9 | 0.001 5 | 0.002 2 |
| 浚326 | 0.002 0 | 0.019 4 | 0.005 9 | 0.003 7 | 0.006 2 | 0.957 8 | 0.005 0 |
| 黄01 | 0.004 1 | 0.004 3 | 0.002 2 | 0.001 6 | 0.003 2 | 0.964 7 | 0.019 9 |
| 370-1 | 0.001 8 | 0.002 0 | 0.010 5 | 0.016 7 | 0.004 7 | 0.954 0 | 0.010 3 |
| 郑22 | 0.001 9 | 0.001 6 | 0.001 8 | 0.001 3 | 0.002 2 | 0.988 9 | 0.002 3 |
| 浚92-8 | 0.003 0 | 0.003 6 | 0.002 7 | 0.002 0 | 0.003 0 | 0.976 2 | 0.009 5 |
| S72702 | 0.003 0 | 0.001 4 | 0.002 2 | 0.001 8 | 0.003 9 | 0.985 4 | 0.002 3 |
| T94 | 0.002 0 | 0.001 3 | 0.001 9 | 0.001 6 | 0.002 0 | 0.989 2 | 0.002 0 |
| 12Y10S-1 | 0.378 4 | 0.010 5 | 0.036 6 | 0.003 0 | 0.021 2 | 0.545 7 | 0.004 6 |
| 12Y10S-3 | 0.089 0 | 0.019 5 | 0.413 8 | 0.152 6 | 0.270 7 | 0.039 0 | 0.015 5 |
| PH1CPS | 0.063 7 | 0.221 5 | 0.032 2 | 0.386 9 | 0.002 6 | 0.002 0 | 0.291 1 |
| ZPH4CV | 0.015 2 | 0.037 2 | 0.283 4 | 0.278 2 | 0.009 6 | 0.334 2 | 0.042 3 |
| 改MS001 | 0.178 4 | 0.327 0 | 0.029 3 | 0.429 7 | 0.004 3 | 0.011 7 | 0.019 5 |
| L16-1 | 0.005 6 | 0.046 4 | 0.014 1 | 0.003 0 | 0.162 6 | 0.360 0 | 0.408 3 |
| 易选-2 | 0.141 7 | 0.279 9 | 0.028 7 | 0.037 5 | 0.010 6 | 0.086 5 | 0.415 1 |
| 12Y10S-3 | 0.015 5 | 0.089 0 | 0.413 8 | 0.270 7 | 0.152 6 | 0.039 0 | 0.019 5 |
| D2-5 | 0.015 0 | 0.009 8 | 0.356 8 | 0.180 2 | 0.186 1 | 0.002 3 | 0.249 8 |
| 543PH62 | 0.003 9 | 0.308 2 | 0.250 2 | 0.229 4 | 0.120 0 | 0.003 2 | 0.085 1 |
| [1] | Duvick D N, Smith J S C, Cooper M. Long term selection in a commercial hybrid maize breeding program[J]. Plant Breeding Review, 2004, 24:109-151. |
| [2] | 陈彦惠, 刘新芝, 彭泽斌, 等. 玉米杂种优势类群和模式的研究Ⅱ玉米自交系优势类群的划分和优势模式初探[J]. 河南农业大学学报, 1995, 29(4):341-347. |
| CHEN Yianhui, LIU Xinzhi, PENG Zebin, et al. Classification of Heterosis Populations and the Construction of Heterosis Models for Maize Inbred Lines[J]. Journal of Henan Agricultural University, 1995, 29(4):341-347. | |
| [3] | 张世煌. 玉米的杂种优势群和杂种优势模式[J]. 作物杂志, 1998,(S1):84-85. |
| ZHANG Shihuang, Heterosis groups and heterosis model in maize[J]. Crops, 1998,(S1):84-85. | |
| [4] | 王懿波, 王振华, 王永普, 等. 中国玉米主要种质杂种优势群的划分及其改良利用[J]. 华北农学报, 1998, 13(1):74-80. |
| WHANG Yibo, WANG Zhenhua, WANG Yongpu, et al. Division,Utilization and the improvement of main germ plasm heterosis of maize in china[J]. Acta Agriculturae Boreali-Sinica, 1998, 13(1):74-80. | |
| [5] |
Reif J C, Melchinger A E, Xia X C, et al. Use of SSRs for establishing heterotic groups in subtropical maize[J]. Theoretical and Applied Genetics, 2003, 107:947-957.
PMID |
| [6] |
Jones E, Chu W C, Ayele M, et al. Development of single nuceotide polymorphism(SNP) marker for use in commercial maize(Zea mays L) germplasm[J]. Molecular Breeding, 2009, 24(2):165-176.
DOI URL |
| [7] | 刘宗华, 汤继华, 王庆东, 等. 河南省主要玉米品种杂种优势利用模式分析[J]. 中国农业科学, 2006, 39(8):1689-1696. |
| LIU Zonghua, TANG Jihua, WANG Qingdong, et al. Analysis of heterotic patterns of maize hybrids used in china's Henan province[J]. Scientia Agricultura Sinica, 2006, 39(8):1689-1696. | |
| [8] | 聂永心, 张丽, 潘光堂, 等. SSR分子标记在玉米杂种优势群划分中的应用[J]. 玉米科学, 2004, 12(3):26-29. |
| NIE Yongxin, ZHANG Li, PAN Guangtang, et al. Application of SSR markers to heterotic grouping of maize inbred lines[J]. Journal of Maize Sciences, 2004, 12(3):26-29. | |
| [9] | 孙友位, 李明顺, 张德贵, 等. 利用SSR标记研究85个玉米自交系的遗传多样性[J]. 玉米科学, 2007, 15(6):19-26. |
| SUN Youwei, LI Mingshun, ZHANG Degui, et al. Determine Genetic Diversity Among 85 Maize Inbred Lines Using SSR Markers[J]. Journal of Maize Sciences, 2007, 15(6):19-26. | |
| [10] | 王凤格, 赵久然, 戴景瑞, 等. 玉米通用SSR核心引物筛选及高通量多重PCR复合扩增体系建立[J]. 科学通报, 2006, 51(23):2738-2746. |
| WANG Fengge, ZHAO Jiuran, DAI Jingrui, et al. Screening of common SSR core primers and establishment of high throughput multiplex PCR amplification system in maize[J]. Chinese Science Bulletin, 2006, 51(23): 2738-2746. | |
| [11] | 刘志斋, 吴迅, 刘海利, 等. 基于40个核心SSR标记揭示的820份中国玉米重要自交系的遗传多样性与群体结构[J]. 中国农业科学, 2012, 45(11):2107-2138. |
| LIU Zhizhai, WU Xun, LIU Haili, et al. Genetic Diversity and Population Structure of Important Chinese Maize Inbred Lines Revealed by 40 Core Simple Sequence Repeats (SSRs)[J]. Scientia Agricultura Sinica, 2012, 45(11):2107-2138. | |
| [12] | 王凤格, 田红丽, 赵久然, 等. 中国328个玉米品种(组合)SSR标记遗传多样性分析[J]. 中国农业科学, 2014, 47(5):856-864. |
| WANG Fengge, TIAN Hongli, ZHAO Jiuran, et al. Genetic Diversity Analysis of 328 Maize Varieties (Hybridized Combinations) Using SSR Markers[J]. Scientia Agricultura Sinica, 2014(5):856-864. | |
| [13] | 梁世浩, 郭晋杰, 贾晓艳, 等. 基于SSR标记和骨干自交系的外引玉米自交系杂种优势群划分[J]. 广东农业科学, 2015, 42(7):122-127. |
| LIANG Shihao, GUO Jinjie, JIA Xiaoyan, et al. Heterotic grouping of exotic maize inbred lines by SSR markers and elite maize inbred lines[J]. Guangdong Agricultural Sciences, 2015, 42(7):122-127. | |
| [14] | 王日新, 盖树鹏, 夏连胜, 等. 玉米自交系亲缘关系的SSR分析[J]. 中国农学通报, 2008, 24(5):100-104. |
| WANG Rixin, GAI Shupeng, XIA Liansheng, et al. Genetic Relationship of Maize Inbred lines Studied by SSR Technology[J]. Chinese Agricultural Science Bulletin, 2008, 24(5):100-104. | |
| [15] | 张微微, 王莉萍, 陈岳, 等. 66个玉米自交系的SSR引物筛选试验初报[J]. 上海农业科技, 2017,(5): 75-76,92. |
| ZHANG Weiwei, WANG Liping, CHEN Yue, et al. Preliminary report on SSR primer screening of 66 Maize inbred Lines[J]. Shanghai Agricultural Science and Technology, 2017,(5):75-76,92. | |
| [16] | 葛建镕, 刘晓鑫, 易红梅, 等. 吉林省42份主推玉米杂交种的遗传分析[J]. 农业与技术, 2008, 28(5):37-42. |
| GE Jianrong, LIU Xiaoxin, YI Hongmei, et al. Genetic analysis of 42 maize hybrids in jilin province[J]. Agriculture & Technology, 2008, 28(5):37-42. | |
| [17] | 郑淑云, 王守才, 刘东占. 利用SSR标记划分玉米自交系杂种优势群的研究[J]. 玉米科学, 2006, 14(5):26-29. |
| ZHENG Shuyun, WANG Shoucai, LIU Dongzhan. Heterotic Grouping of Maize Inbred Lines Classified by Using SSR Markers[J]. Journal of Maize Sciences, 2006, 14(5):26-29. | |
| [18] | 赵久然, 李春辉, 宋伟, 等. 利用SSR标记解析京科968等系列玉米品种的杂优模式[J]. 玉米科学, 2017, 25(5):1-8. |
| ZHAO Jiuran, LI Chunhui, SONG Wei, et al. Elaboration of Heterotic Pattern in a Series of Maize Varieties by SSR Markers[J]. Journal of Maize Sciences, 2017, 25(5):1-8. | |
| [19] | 卢振宇, 李明顺, 谢传晓, 等. 玉米叶片DNA快速提取方法改进研究[J]. 玉米科学, 2008, 16(2):50-53. |
| LU Zhenyu, LI Mingshun, XIE Chuanxiao, et al. An Improved Study on Rapid DNA Extraction Method from Young Leaves of Maize[J]. Journal of Maize Sciences, 2008, 16(2):50-53. | |
| [20] | 李玥, 王汉宁, 王爱听, 等. 利用SSR标记对126份玉米自交系种质类群划分的初探[J]. 作物杂志, 2013,(4):38-42. |
| LI Yue, WANG Hanning, WANG Aiting, et al. Classification of 126 Inbred Lines Using SSR Markers[J]. Crops, 2013,(4):38-42. | |
| [21] | Liu K, Muse S V. Power Marker: an integrated analysis environment for genetic marker analysis[J]. Bioinformatics, 2005(9):2128-2129. |
| [22] |
Kaeuffer R D, Rale Coltman D W, et al. Detecting population structure using STRUCTURE software: effect of background linkage disequilibrium[J]. Heredity, 2007, 99(4):374-80.
PMID |
| [23] |
Zhang R, Xu G, Li J,. et al. Patterns of genomic variation in Chinese maize inbred lines and implications for genetic improvement[J]. Theoretical and Applied Genetics, 2018, 131:1207-1221.
DOI URL |
| [24] | 赵久然, 李春辉, 宋伟, 等. 基于SNP芯片揭示中国玉米育种种质的遗传多样性与群体遗传结构[J]. 中国农业科学, 2018, 51(4):626-634. |
| ZHIAO Jiuran, LI Chunhui, SONG Wei, et al. Genetic Diversity and Population Structure of Important Chinese Maize Breeding Germplasm Revealed by SNP-Chips[J]. Scientia Agricultura Sinica, 2018, 51(4):626-634. |
| [1] | 王挺, 张力, 张凡凡, 黄嵘峥, 李肖, 张玉琳, 陈永成, 赵建涛, 马春晖. 适合青贮的玉米品种生产性能筛选及营养价值评价[J]. 新疆农业科学, 2023, 60(7): 1596-1605. |
| [2] | 陈占辉, 孙强, 任姣姣, 黄博文, 许加波, 杨杰, 吴鹏昊. 玉米叶宽的QTL定位及全基因组选择分析[J]. 新疆农业科学, 2023, 60(7): 1606-1613. |
| [3] | 蓝陈仪航, 姚禹博, 周俊祥, 付开赟, 丁新华, 尹晓辉, 刘文, 王娜, 郭文超, 邓建宇. 亚洲玉米螟性信息素鉴定及其应用研究进展[J]. 新疆农业科学, 2023, 60(7): 1614-1622. |
| [4] | 邵盘霞, 赵准, 邵武奎, 郝晓燕, 高升旗, 李建平, 胡文冉, 黄全生. 玉米ZmCDPK22基因在干旱胁迫下的表达分析[J]. 新疆农业科学, 2023, 60(6): 1372-1378. |
| [5] | 陆晏天, 桑志勤, 徐灿, 张力, 夏春兰, 王友德, 李伟, 陈树宾. 历年新疆和宁夏审定玉米品种主要性状的演化及品种审定现状分析[J]. 新疆农业科学, 2023, 60(6): 1379-1388. |
| [6] | 杨明花, 刘强, 廖必勇, 彭云承, 布阿依夏木·那曼提, 达吾来·杰克山. 不完全双列杂交玉米组合抗倒伏综合评价[J]. 新疆农业科学, 2023, 60(4): 832-840. |
| [7] | 周广威, 韩登旭, 朱琦, 张少民. 耐低磷新疆春玉米基因型筛选及其磷效率[J]. 新疆农业科学, 2023, 60(4): 847-856. |
| [8] | 陈果, 郝晓燕, 高升旗, 胡文冉, 赵准, 黄全生. 玉米钙依赖蛋白激酶全基因组鉴定及抗旱表达分析[J]. 新疆农业科学, 2023, 60(4): 857-864. |
| [9] | 董秀丽, 韩登旭, 杨杰, 阿布来提·阿布拉, 戴爱梅, 李俊杰, 王业建, 刘俊, 郗浩江, 梁晓玲, 李铭东. 密植条件下玉米主要农艺性状的综合性分析[J]. 新疆农业科学, 2023, 60(4): 865-871. |
| [10] | 侯良忠, 郭同军, 张俊瑜, 苏玲玲, 古再丽努尔·艾麦提, 温小燕, 朱晓芳, 杨建中, 王文奇. 不同比例籽用西葫芦皮瓤与玉米秸秆混贮效果评价[J]. 新疆农业科学, 2023, 60(3): 567-573. |
| [11] | 段燕燕, 胡静, 祁炳琴, 潘志远, 吴昊楠, 勾玲. 正反交对玉米杂交种茎秆抗倒伏性能及种植密度的响应[J]. 新疆农业科学, 2023, 60(12): 2949-2961. |
| [12] | 张伟, 靳范, 李谦绪, 张俊三, 翟修萍, 王善博. 玉米籽粒联合收获机清选装置优化设计与试验[J]. 新疆农业科学, 2023, 60(12): 3102-3112. |
| [13] | 唐怀君, 谢小清, 张磊, 孙宝成, 杨杰, 刘成. 283份玉米田间抗旱性鉴定与筛选[J]. 新疆农业科学, 2023, 60(11): 2687-2693. |
| [14] | 谢小清, 唐怀君, 张磊, 孙宝成, 刘成. 玉米果穗性状及其抗旱性随灌水量的变化规律[J]. 新疆农业科学, 2023, 60(10): 2412-2418. |
| [15] | 魏勇, 高雨, 杨敏, 许子豪, 任万平. 饲喂蒸汽压片玉米对新疆褐牛产肉性能及肝脏营养物质代谢的影响[J]. 新疆农业科学, 2023, 60(10): 2583-2589. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||